5.5: Alineación regional basada en genes
- Page ID
- 54163
Una forma alternativa de alinear múltiples genomas ancla segmentos genómicos basados en los genes que contienen, y utiliza la correspondencia de genes para resolver las regiones correspondientes en cada par de especies. Luego se construye un alineamiento a nivel de nucleótidos basado en métodos descritos anteriormente en cada región conservada multiplicada.
Debido a que no todas las regiones tienen correspondencia uno a uno y la secuencia no es estática, esto es más difícil: los genes experimentan divergencia, duplicación y pérdidas y genomas completos sufren reordenamientos. Para ayudar a superar estos desafíos, los investigadores analizan la similitud de aminoácidos de los pares de genes en los genomas y la ubicación de los genes dentro de cada genoma.
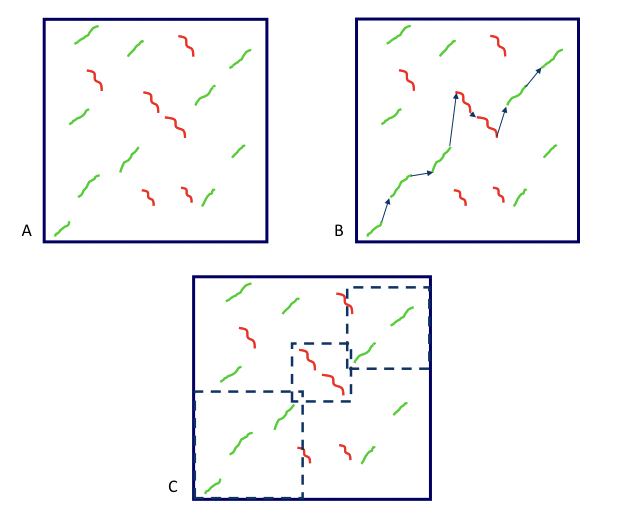
Figura 5.18: Los pasos para ejecutar el algoritmo SLAGAN son A. Encontrar todas las alineaciones locales, B. Construir un mapa de homología aproximada, y C. alinear globalmente las partes consistentes usando el algoritmo LAGAN regular
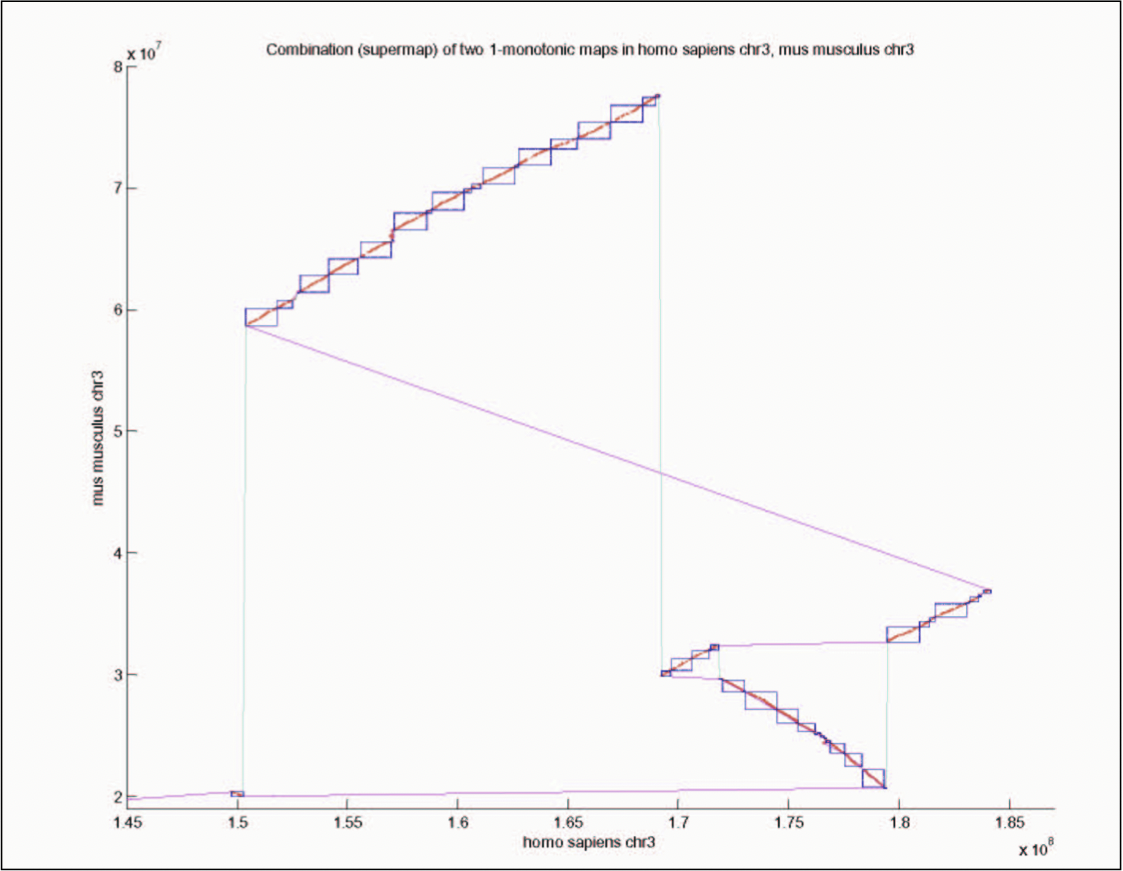
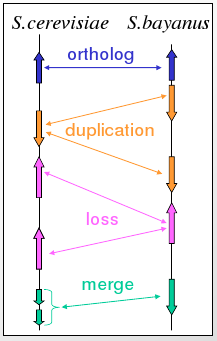
Figura 5.20: Gráfica de correspondencia génica de S. cerevisae y S. bayanus.
La correspondencia génica puede representarse mediante una gráfica bipartita ponderada con nodos que representan genes con coordenadas y bordes que representan similitud de secuencia ponderada (Figura 5.20). Las relaciones ortólogas son coincidencias uno a uno y las relaciones parálogas son coincidencias de uno a muchos o de muchos a muchos. La gráfica se simplifica primero eliminando bordes espurios y luego los bordes se seleccionan en base a la información disponible, como bloques de orden génico conservado y similitud de secuencia de proteínas.
El algoritmo Best Unambiguous Subgroups (BUS) se puede utilizar entonces para resolver la correspondencia de genes y regiones. BUS extiende el concepto de mejores aciertos bidireccionales y utiliza refinamiento iterativo con un umbral relativo creciente. Utiliza la conectividad completa de gráficos bipartitos con similitud de aminoácidos integrada e información de orden de genes.
¿Sabías?
La gráfica bipartita es una gráfica cuyos vértices se pueden dividir en dos conjuntos disjuntos U y V de tal manera que cada borde conecta un vértice en U a un vértice en V.

Figura 5.21: Ilustración de la correspondencia génica para el Cromosoma VI de S.cerevisiae (250-300pb).
En el ejemplo de una correspondencia génica correctamente resuelta de S.cerevisiae con otras tres especies relacionadas, más del 90% de los genes tuvieron una correspondencia uno a uno y se identificaron regiones y familias de proteínas de cambio rápido.


