5.3: Modelando la evolución de los caracteres correlacionados
- Page ID
- 53747
Podemos modelar la evolución de múltiples caracteres continuos (potencialmente correlacionados) usando un modelo de movimiento browniano multivariado. Este modelo es similar al movimiento browniano univariado (ver capítulo 3), pero puede modelar la evolución de muchos personajes al mismo tiempo. Al igual que con el movimiento browniano univariado, los valores de rasgo cambian aleatoriamente tanto en dirección como en distancia en cualquier intervalo de tiempo. Aquí, sin embargo, estos cambios se extraen de distribuciones normales multivariadas 2. El movimiento browniano multivariado puede abarcar la situación en la que cada personaje evoluciona independientemente el uno del otro, pero también puede describir situaciones en las que los personajes evolucionan de manera correlacionada.
Podemos describir el movimiento browniano multivariado con un conjunto de parámetros que son descritos por a, un vector de medios filogenéticos para un conjunto de r caracteres:
(eq. 5.1)
\[ \mathbf{a} = \begin{bmatrix} \bar{z}_1 (0) & \bar{z}_2 (0) & \dots & \bar{z}_r (0)\\ \end{bmatrix} \]
Este vector representa el punto de partida en el espacio r -dimensional para nuestro paseo aleatorio. En el contexto de los métodos comparativos, se trata de las medidas de carácter para el linaje en la raíz del árbol. Adicionalmente, tenemos una matriz de tasa evolutiva R:
(eq. 5.2)
\[ \mathbf{R} = \begin{bmatrix} \sigma_1^2 & \sigma_{21} & \dots & \sigma_{n1}\\ \sigma_{21} & \sigma_2^2 & \dots & \vdots\\ \vdots & \vdots & \ddots & \vdots\\ \sigma_{1n} & \dots & \dots & \sigma_{rn}^2\\ \end{bmatrix}\]
Aquí, el parámetro de tasa para cada eje (σ i 2) es a lo largo de la diagonal de la matriz. Los elementos fuera de la diagonal representan covarianzas evolutivas entre pares de ejes (nótese que σ i j = σ j i). Vale la pena señalar que cada personaje individual evoluciona bajo un proceso de movimiento browniano. Las covarianzas entre personajes, sin embargo, potencialmente hacen que este modelo sea distinto de uno en el que cada personaje evoluciona independientemente de todos los demás (Figura 5.2).
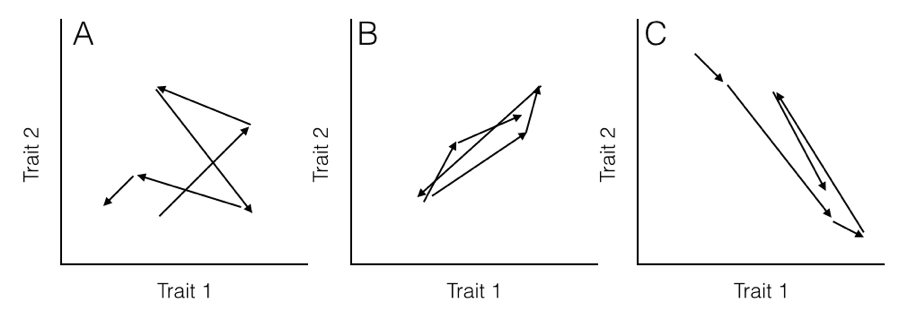
Cuando tienes datos para múltiples caracteres continuos en muchas especies junto con un árbol filogenético, puedes ajustar un modelo de movimiento browniano multivariado a los datos, como se discute en el Capítulo 3.
Para calcular la probabilidad, podemos usar el hecho de que, bajo nuestro modelo de movimiento browniano multivariante, la distribución conjunta de todos los rasgos en todas las especies tiene una distribución normal multivariada. Siguiendo el Capítulo 3, encontramos la matriz varianza-covarianza que describe ese modelo combinando las dos matrices R y C en una sola matriz grande usando el producto Kroeneker:
(eq. 5.3)
V = R C
Esta matriz V es n r × n r. Luego podemos sustituir V por C en la ecuación (4.5) para calcular la probabilidad:
(eq. 5.4)
\[ L(\mathbf{x}_{nr} | \mathbf{a}, \mathbf{R}, \mathbf{C}) = \frac {e^{-1/2 (\mathbf{x}_{nr}- \mathbf{D} \cdot \mathbf{a})^\intercal (\mathbf{V})^{-1} (\mathbf{x}_nr-\mathbf{D} \cdot \mathbf{a})}} {\sqrt{(2 \pi)^{nm} det(\mathbf{V})}} \]
Aquí D es una matriz de diseño n r × r donde cada elemento D i j es 1 si (j − 1) ⋅ n < i ≤ j ⋅ n y 0 de lo contrario. x n r es un solo vector con todos los valores de rasgo para todas las especies, enumerados de manera que los primeros n elementos en el vector son el rasgo 1, los siguientes n son para el rasgo 2, y así sucesivamente:
(eq. 5.5)
\[ \mathbf{x}_{nr} = \begin{bmatrix} x_{11} & x_{12} & \dots & x_{1n} & x_{21} & \dots & x_{nr}\\ \end{bmatrix} \]
Podemos encontrar el valor de la verosimilitud en su máximo calculando L (x n r | a, R, C) usando la ecuación 5.4 y una rutina de optimización para encontrar el MLE.
Alternativamente, se puede calcular esta solución MLE directamente. Las ecuaciones para estimar $\ hat {\ mathbf {a}} $ (el vector estimado de medias filogenéticas para todos los caracteres) y $\ hat {\ mathbf {R}} $ (la matriz de tasa evolutiva estimada) son (Revell y Harmon 2008, Hohenlohe y Arnold (2008)):
(eq. 5.6)
\[ \hat{\mathbf{a}} = [(\mathbf{1}^\intercal \mathbf{C}^{-1} \mathbf{1})^{-1}(\mathbf{1}^\intercal \mathbf{C}^{-1} \mathbf{X})]^\intercal \]
(eq. 5.7)
\[ \hat{\mathbf{R}} = \frac{(\mathbf{X} - \mathbf{1} \mathbf{\hat{a}})^\intercal \mathbf{C}^{-1} (\mathbf{X} - \mathbf{1} \mathbf{\hat{a}})}{n} \]
Observe aquí que usamos X para denotar la matriz n (especie) × r (rasgos) de todos los rasgos en todas las especies. Obsérvese la similitud entre estas ecuaciones multivariadas (5.6 y 5.7) y sus equivalentes univariados (ecuaciones 4.6 y 4.7).


