5.2: Reparación de ADN
- Page ID
- 53550
Mantener la integridad de la información de la célula: Reparación del ADN
En la última sección se consideraron las formas en que las células afrontan los desafíos asociados a replicar su ADN, un proceso vital para todas las células. Es evidente que si el ADN es la copia maestra de instrucciones para un organismo, entonces es importante no cometer errores al copiar el ADN para pasarlo a nuevas células. Aunque la corrección de pruebas por ADN polimerasas aumenta en gran medida la precisión de la replicación, existen mecanismos adicionales en las células para garantizar aún más que el ADN recién replicado sea una copia fiel del original, y también para reparar el daño al ADN durante la vida normal de una célula.
Todo el ADN sufre daños a lo largo del tiempo, por la exposición a la radiación ultravioleta y otras radiaciones, así como por diversos químicos en el medio ambiente. Incluso las reacciones químicas que ocurren naturalmente dentro de las células pueden dar lugar a compuestos que pueden dañar el ADN. Como ya sabrás, incluso cambios menores en la secuencia del ADN, como las mutaciones puntuales, a veces pueden tener consecuencias de largo alcance. De igual manera, los daños no reparados causados por la radiación, los químicos ambientales o incluso la química celular normal pueden interferir con la transmisión precisa de la información en el ADN. Mantener la integridad del “plano” de la célula es de vital importancia y esto se refleja en los numerosos mecanismos que existen para reparar errores y daños en el ADN.

Reparación de desajuste post-replicativo
Anteriormente discutimos la corrección de pruebas por ADN polimerasas durante la replicación. ¿La corrección elimina todos los errores cometidos durante la replicación? No. Si bien la corrección de pruebas reduce significativamente la tasa de error, no todos los errores son fijados sobre la marcha por las ADN polimerasas. Qué mecanismos existen para corregir los errores de replicación que se pierden por la función correctora de ADN polimerasas.
Los errores que se deslizan al corregir durante la replicación se pueden corregir mediante un mecanismo llamado reparación de desajustes. Si bien la tasa de error de replicación del ADN es de aproximadamente uno en\(10^7\) nucleótidos en ausencia de reparación de desapareamientos, esto se reduce aún más cien veces a uno en\) 10^9\) nucleótidos cuando la reparación de desapareamientos es funcional.
Cuáles son las tareas a las que se enfrenta un sistema de reparación de desajustes. Debe:
- Escanee ADN recién hecho para ver si hay bases mal ventiladas (por ejemplo, una G emparejada con una T)
- Identificar y cortar la región del desajuste.
- Llenar correctamente el vacío creado por la escisión de la región de desajuste.
Es importante destacar que el sistema de reparación de desapareamientos debe tener un medio para distinguir la cadena de ADN recién hecha de la cadena molde, si los errores de replicación se van a corregir correctamente. En otras palabras, cuando el sistema de reparación de desajustes encuentra un mal juego A-G, por ejemplo, debe saber si la A debe ser removida y reemplazada por una C o si la G debe ser removida y reemplazada por una T.
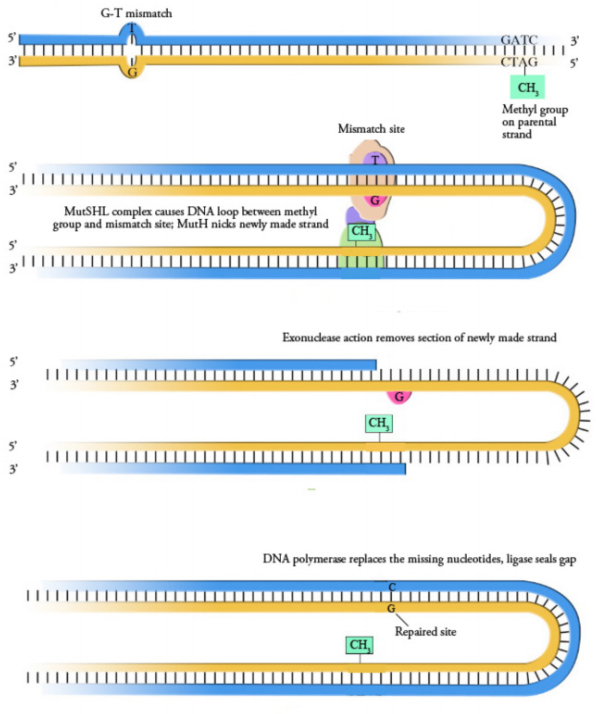
La reparación de desapareamientos ha sido bien estudiada en bacterias y se han identificado las proteínas involucradas. Los eucariotas tienen un sistema de reparación de desajustes que repara no solo los desajustes de base única sino también las inserciones y eliminaciones. En las bacterias, las proteínas reparadoras de desapareamientos son codificadas por un grupo de genes conocidos colectivamente como genes mut. Algunos de los componentes más importantes de la maquinaria de reparación de desapareamientos son las proteínas MuTs, L y H. MuTs actúa para reconocer el desapareamiento, mientras que MutL y MuTH son reclutados en el sitio de desapareamientos por la unión de Mut S, para ayudar a cortar la región que contiene el desapare Una ADN polimerasa y ligasa llenan el hueco y unen los extremos, respectivamente.
Pero, ¿cómo distingue el sistema de reparación de desajustes entre las hebras originales y las nuevas de ADN? En bacterias, la existencia de un sistema que metila el ADN en las secuencias GATC es la solución a este problema. E. coli tiene una enzima que agrega grupos metilo a las adeninas en las secuencias GATC. El ADN recién replicado carece de estametilación y, por lo tanto, puede distinguirse de la cadena molde, que está metilada. En la Figura\(\PageIndex{2}\), la cadena molde mostrada en amarillo está metilada en las secuencias GATC. Las proteínas reparadoras de desapareamientos reemplazan selectivamente la hebra carente de metilación, mostrada en azul en la figura, asegurando así que son errores en la cadena recién hecha los que se eliminan y reemplazan. Debido a que la metilación es el criterio que permite que el sistema de reparación de desapareamientos elija la cadena que se repara, el sistema de reparación de desapareamientos bacterianos se describe como dirigido
Las células eucariotas no utilizan este mecanismo para distinguir la nueva cadena de la plantilla, y aún no se entiende cómo el sistema de reparación de desapareamientos en eucariotas “sabe” qué cadena reparar.
Sistemas para Reparar Daños al ADN
En la sección anterior discutimos los errores cometidos cuando se copia el ADN, donde se inserta la base incorrecta durante la síntesis de la nueva cadena. Pero incluso el ADN que no se está replicando puede dañarse o mutarse. Este tipo de daños no están asociados con la replicación del ADN, sino que pueden ocurrir en cualquier momento.
¿Qué causa daño al ADN? Algunas de las principales causas de daño al ADN son:
- Radiación (por ejemplo, rayos UV en la luz solar, en cabinas de bronceado)
- Exposición a productos químicos dañinos (como benzopireno en los gases de escape de los automóviles y el humo del cigarrillo)
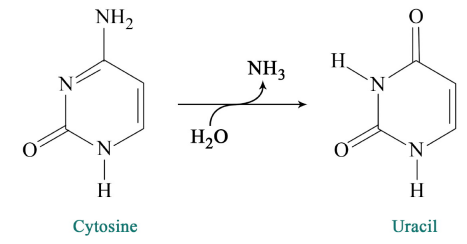
- Reacciones químicas dentro de la célula (como la desaminación de citosina para dar uracilo).
Esto significa que el ADN en tus células es vulnerable al daño simplemente por tipos normales de acciones, como caminar al aire libre, estar en el tráfico o por las transformaciones químicas que ocurren en cada célula como parte de sus actividades cotidianas. (Naturalmente, el daño es mucho peor en situaciones donde la exposición a la radiación o productos químicos dañinos es mayor, como cuando las personas usan repetidamente camas de bronceado o fuman).
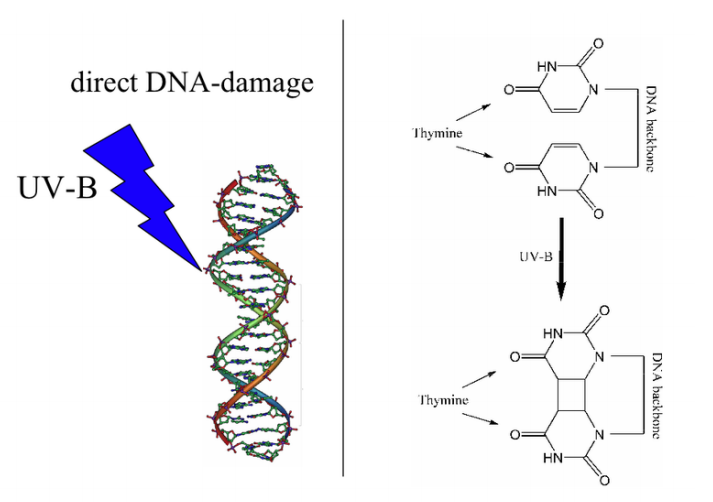
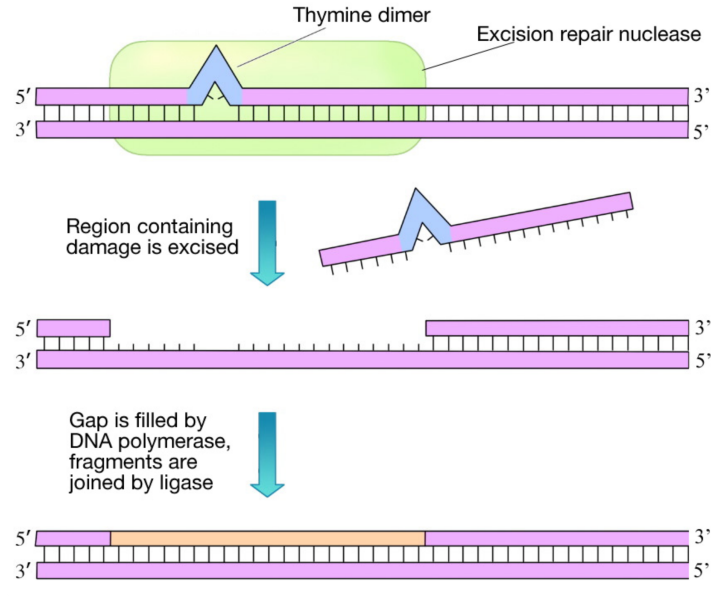
¿Qué tipo de daño causan estos agentes? La radiación puede causar diferentes tipos de daño al ADN. En ocasiones, como con gran parte del daño que producen los rayos UV, dos bases de pirimidina adyacentes en el ADN se reticularán para formar dímeros de pirimidina (nótese que estamos hablando de dos bases de pirimidina vecinas en la misma cadena de ADN). Esto se ilustra en la figura de la página anterior donde dos timinas adyacentes en una sola cadena de ADN se reticulan para formar un dímero de timina. La radiación también puede causar roturas en la columna vertebral del ADN.
Químicos como el benzopireno pueden unirse a bases, formando aductos de ADN voluminosos en los que grandes grupos químicos están unidos a bases en el ADN. La formación de aductos químicos puede distorsionar físicamente la hélice del ADN, dificultando que las ADN y ARN polimerasas copien esas regiones del ADN.
Las reacciones químicas que ocurren dentro de las células pueden provocar que las citosinas en el ADN se desaminen a uracilo, como se muestra en la Figura\(\PageIndex{3}\).
Otros tipos de daños en esta categoría incluyen la formación de bases oxidadas como la 8-oxo-guanina. Estos en realidad no cambian la estructura física de la hélice del ADN, pero pueden causar problemas porque el uracilo y la 8-oxo-guanina se emparejan con bases diferentes a la citosina o guanina originales, lo que lleva a mutaciones en la siguiente ronda de replicación.
¿Cómo reparan las células tal daño? Las células tienen varias formas de eliminar los tipos de daño descritos anteriormente, siendo la reparación por escisión una estrategia común. Reparación por escisión es un término general para el corte y resíntesis de la región dañada del ADN. Hay un par de variedades de reparación por escisión:
Reparación de Escisión de Nucleótidos (NER)
Este sistema corrige los daños causados por productos químicos, así como los daños UV. Como se muestra en la figura de la página anterior, en la reparación por escisión de nucleótidos, se reconoce el daño y se realiza un corte a ambos lados de la región dañada por una enzima llamada excinucleasa (mostrada en verde). Luego se elimina una porción corta de la cadena de ADN que contiene el daño y una ADN polimerasa rellena el hueco con los nucleótidos apropiados. El ADN recién hecho se une al resto de la cadena principal del ADN por la enzima ADN ligasa. En E. coli, la NER es realizada por un grupo de proteínas codificadas por los genes uvrabC. Como puede ver, NER es similar, en principio, a la reparación de desajustes. Sin embargo, en NER, la distorsión de la hélice, causada por el daño en el ADN, indica claramente qué hebra del ADN necesita ser removida y reemplazada.
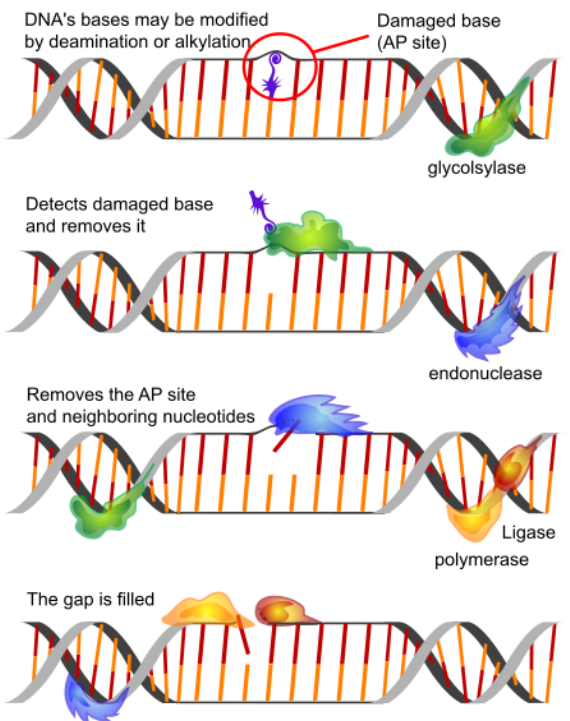
Reparación de Escisión Base (BER)
BER trata situaciones como la desaminación de citosina a uracilo. Como se señaló anteriormente, las citosinas en el ADN a veces sufren desaminación para formar la base uracilo.
Debido a que las citosinas se emparejan con guaninas y los uracilos se emparejan con adenina, la conversión de citosina en uracilo en el ADN conduciría a la inserción de una A en la cadena recién replicada en lugar de la G que debería haber entrado frente a una C. Para evitar que esto suceda, los uracilos se eliminan del ADN por base reparación por escisión.
En la reparación por escisión de bases, primero se elimina una sola base del ADN, seguido de la eliminación de una región del ADN que rodea la base faltante. Luego se repara la brecha.
La eliminación del uracilo del ADN se logra mediante la enzima uracilo ADN glicosilasa, que rompe el enlace entre el uracilo y el azúcar en el nucleótido.
La eliminación de la base de uracilo crea un hueco llamado sitio apirimidínico (sitio AP). La presencia del sitio AP desencadena la actividad de una endonucleasa AP que corta el esqueleto del ADN.
Luego se elimina y reemplaza una región corta del ADN que rodea el sitio del uracilo original.