4.5: Espectroscopia ultravioleta y visible
- Page ID
- 72065
\( \newcommand{\vecs}[1]{\overset { \scriptstyle \rightharpoonup} {\mathbf{#1}} } \)
\( \newcommand{\vecd}[1]{\overset{-\!-\!\rightharpoonup}{\vphantom{a}\smash {#1}}} \)
\( \newcommand{\id}{\mathrm{id}}\) \( \newcommand{\Span}{\mathrm{span}}\)
( \newcommand{\kernel}{\mathrm{null}\,}\) \( \newcommand{\range}{\mathrm{range}\,}\)
\( \newcommand{\RealPart}{\mathrm{Re}}\) \( \newcommand{\ImaginaryPart}{\mathrm{Im}}\)
\( \newcommand{\Argument}{\mathrm{Arg}}\) \( \newcommand{\norm}[1]{\| #1 \|}\)
\( \newcommand{\inner}[2]{\langle #1, #2 \rangle}\)
\( \newcommand{\Span}{\mathrm{span}}\)
\( \newcommand{\id}{\mathrm{id}}\)
\( \newcommand{\Span}{\mathrm{span}}\)
\( \newcommand{\kernel}{\mathrm{null}\,}\)
\( \newcommand{\range}{\mathrm{range}\,}\)
\( \newcommand{\RealPart}{\mathrm{Re}}\)
\( \newcommand{\ImaginaryPart}{\mathrm{Im}}\)
\( \newcommand{\Argument}{\mathrm{Arg}}\)
\( \newcommand{\norm}[1]{\| #1 \|}\)
\( \newcommand{\inner}[2]{\langle #1, #2 \rangle}\)
\( \newcommand{\Span}{\mathrm{span}}\) \( \newcommand{\AA}{\unicode[.8,0]{x212B}}\)
\( \newcommand{\vectorA}[1]{\vec{#1}} % arrow\)
\( \newcommand{\vectorAt}[1]{\vec{\text{#1}}} % arrow\)
\( \newcommand{\vectorB}[1]{\overset { \scriptstyle \rightharpoonup} {\mathbf{#1}} } \)
\( \newcommand{\vectorC}[1]{\textbf{#1}} \)
\( \newcommand{\vectorD}[1]{\overrightarrow{#1}} \)
\( \newcommand{\vectorDt}[1]{\overrightarrow{\text{#1}}} \)
\( \newcommand{\vectE}[1]{\overset{-\!-\!\rightharpoonup}{\vphantom{a}\smash{\mathbf {#1}}}} \)
\( \newcommand{\vecs}[1]{\overset { \scriptstyle \rightharpoonup} {\mathbf{#1}} } \)
\( \newcommand{\vecd}[1]{\overset{-\!-\!\rightharpoonup}{\vphantom{a}\smash {#1}}} \)
\(\newcommand{\avec}{\mathbf a}\) \(\newcommand{\bvec}{\mathbf b}\) \(\newcommand{\cvec}{\mathbf c}\) \(\newcommand{\dvec}{\mathbf d}\) \(\newcommand{\dtil}{\widetilde{\mathbf d}}\) \(\newcommand{\evec}{\mathbf e}\) \(\newcommand{\fvec}{\mathbf f}\) \(\newcommand{\nvec}{\mathbf n}\) \(\newcommand{\pvec}{\mathbf p}\) \(\newcommand{\qvec}{\mathbf q}\) \(\newcommand{\svec}{\mathbf s}\) \(\newcommand{\tvec}{\mathbf t}\) \(\newcommand{\uvec}{\mathbf u}\) \(\newcommand{\vvec}{\mathbf v}\) \(\newcommand{\wvec}{\mathbf w}\) \(\newcommand{\xvec}{\mathbf x}\) \(\newcommand{\yvec}{\mathbf y}\) \(\newcommand{\zvec}{\mathbf z}\) \(\newcommand{\rvec}{\mathbf r}\) \(\newcommand{\mvec}{\mathbf m}\) \(\newcommand{\zerovec}{\mathbf 0}\) \(\newcommand{\onevec}{\mathbf 1}\) \(\newcommand{\real}{\mathbb R}\) \(\newcommand{\twovec}[2]{\left[\begin{array}{r}#1 \\ #2 \end{array}\right]}\) \(\newcommand{\ctwovec}[2]{\left[\begin{array}{c}#1 \\ #2 \end{array}\right]}\) \(\newcommand{\threevec}[3]{\left[\begin{array}{r}#1 \\ #2 \\ #3 \end{array}\right]}\) \(\newcommand{\cthreevec}[3]{\left[\begin{array}{c}#1 \\ #2 \\ #3 \end{array}\right]}\) \(\newcommand{\fourvec}[4]{\left[\begin{array}{r}#1 \\ #2 \\ #3 \\ #4 \end{array}\right]}\) \(\newcommand{\cfourvec}[4]{\left[\begin{array}{c}#1 \\ #2 \\ #3 \\ #4 \end{array}\right]}\) \(\newcommand{\fivevec}[5]{\left[\begin{array}{r}#1 \\ #2 \\ #3 \\ #4 \\ #5 \\ \end{array}\right]}\) \(\newcommand{\cfivevec}[5]{\left[\begin{array}{c}#1 \\ #2 \\ #3 \\ #4 \\ #5 \\ \end{array}\right]}\) \(\newcommand{\mattwo}[4]{\left[\begin{array}{rr}#1 \amp #2 \\ #3 \amp #4 \\ \end{array}\right]}\) \(\newcommand{\laspan}[1]{\text{Span}\{#1\}}\) \(\newcommand{\bcal}{\cal B}\) \(\newcommand{\ccal}{\cal C}\) \(\newcommand{\scal}{\cal S}\) \(\newcommand{\wcal}{\cal W}\) \(\newcommand{\ecal}{\cal E}\) \(\newcommand{\coords}[2]{\left\{#1\right\}_{#2}}\) \(\newcommand{\gray}[1]{\color{gray}{#1}}\) \(\newcommand{\lgray}[1]{\color{lightgray}{#1}}\) \(\newcommand{\rank}{\operatorname{rank}}\) \(\newcommand{\row}{\text{Row}}\) \(\newcommand{\col}{\text{Col}}\) \(\renewcommand{\row}{\text{Row}}\) \(\newcommand{\nul}{\text{Nul}}\) \(\newcommand{\var}{\text{Var}}\) \(\newcommand{\corr}{\text{corr}}\) \(\newcommand{\len}[1]{\left|#1\right|}\) \(\newcommand{\bbar}{\overline{\bvec}}\) \(\newcommand{\bhat}{\widehat{\bvec}}\) \(\newcommand{\bperp}{\bvec^\perp}\) \(\newcommand{\xhat}{\widehat{\xvec}}\) \(\newcommand{\vhat}{\widehat{\vvec}}\) \(\newcommand{\uhat}{\widehat{\uvec}}\) \(\newcommand{\what}{\widehat{\wvec}}\) \(\newcommand{\Sighat}{\widehat{\Sigma}}\) \(\newcommand{\lt}{<}\) \(\newcommand{\gt}{>}\) \(\newcommand{\amp}{&}\) \(\definecolor{fillinmathshade}{gray}{0.9}\)Mientras que la interacción con la luz infrarroja hace que las moléculas experimenten transiciones vibracionales, la longitud de onda más corta, la radiación de mayor energía en el rango UV (200-400 nm) y visible (400-700 nm) del espectro electromagnético hace que muchas moléculas orgánicas experimenten transiciones electrónicas. Lo que esto significa es que cuando la energía de la luz UV o visible es absorbida por una molécula, uno de sus electrones salta de un orbital molecular de menor energía a un orbital molecular de mayor energía.
Transiciones electrónicas
Tomemos como nuestro primer ejemplo el caso simple del hidrógeno molecular, H 2. Como recordará de la sección 2.1A, la imagen orbital molecular para la molécula de hidrógeno consiste en un enlace σ MO y un antienlace de mayor energía σ * MO. Cuando la molécula está en el estado fundamental, ambos electrones se emparejan en el orbital de enlace de menor energía, este es el Orbital Molecular Ocupado más Alto (HOMO). El orbital antiunión σ *, a su vez, es el Orbital Molecular Desocupado Más Bajo (LUMO).

Si la molécula se expone a luz de una longitud de onda con energía igual a Δ E, la brecha de energía HOMO-LUMO, esta longitud de onda será absorbida y la energía utilizada para chocar uno de los electrones del HOMO al LUMO —en otras palabras, del orbital σ al σ *. Esto se conoce como una transición σ - σ *. Δ E para esta transición electrónica es de 258 kcal/mol, correspondiente a la luz con una longitud de onda de 111 nm.
Cuando una molécula de doble enlace como el eteno (nombre común etileno) absorbe la luz, se somete a una transición π - π *. Debido a que los huecos de energía π - π * son más estrechos que los huecos σ - σ *, el eteno absorbe la luz a 165 nm, una longitud de onda más larga que el hidrógeno molecular.

Las transiciones electrónicas tanto del hidrógeno molecular como del eteno son demasiado energéticas para ser registradas con precisión por espectrofotómetros UV estándar, que generalmente tienen un rango de 220 — 700 nm. Donde la espectroscopia UV-Vis se vuelve útil para la mayoría de químicos orgánicos y biológicos es en el estudio de moléculas con\(\pi\) sistemas conjugados. En estos grupos, la brecha de energía para las transiciones π - π * es menor que para los dobles enlaces aislados, y así la longitud de onda absorbida es más larga. Las moléculas o partes de moléculas que absorben la luz fuertemente en la región UV-Vis se denominan cromóforos.
Revisemos la imagen MO para 1,3-butadieno, el sistema conjugado más simple. Recordemos que podemos dibujar un diagrama que muestre los cuatro pi MO que resultan de combinar los cuatro orbitales atómicos de 2p z. Los dos orbitales inferiores se unen, mientras que los dos superiores son antiadherentes.
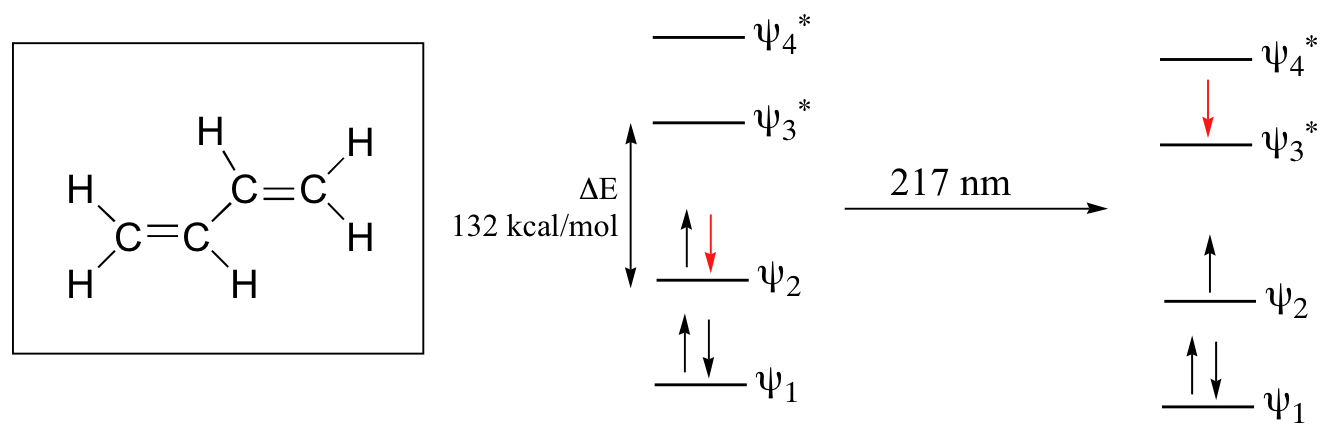
Comparando esta imagen MO con la del eteno, nuestro ejemplo aislado de enlace pi, vemos que la brecha de energía HOMO-LUMO es de hecho más pequeña para el sistema conjugado. El 1,3-butadieno absorbe la luz UV con una longitud de onda de 217 nm.
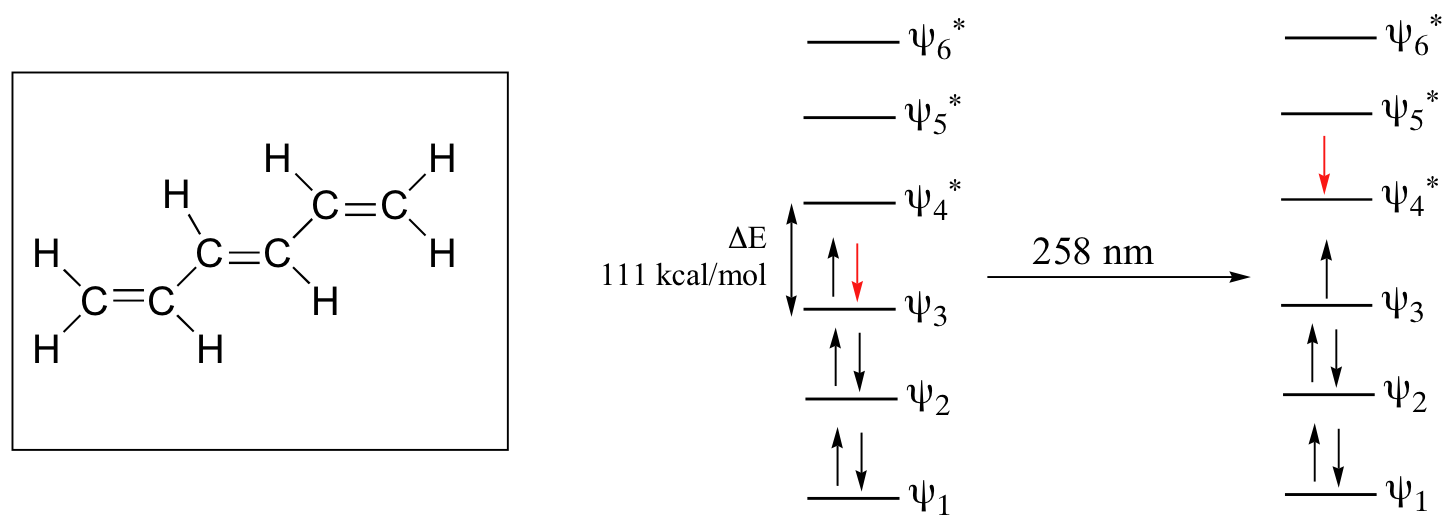
A medida que los sistemas pi conjugados se hacen más grandes, la brecha de energía para una transición π - π * se vuelve cada vez más estrecha, y la longitud de onda de la luz absorbida correspondientemente se hace La absorbancia debida a la transición π - π * en 1,3,5-hexatrieno, por ejemplo, ocurre a 258 nm, correspondiente a una Δ E de 111 kcal/mol.
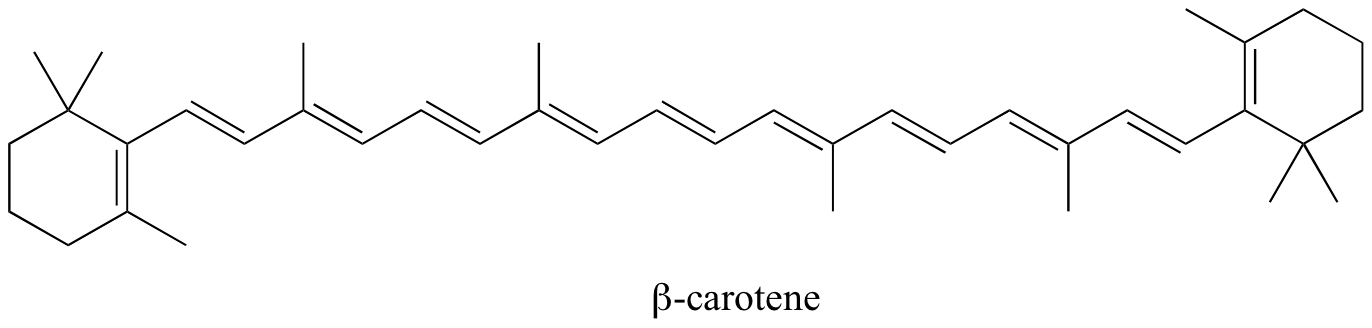
En las moléculas con sistemas pi extendidos, la brecha de energía HOMO-LUMO se vuelve tan pequeña que la absorción ocurre en la región visible y no en la región UV del espectro electromagnético. El betacaroteno, con su sistema de 11 dobles enlaces conjugados, absorbe la luz con longitudes de onda en la región azul del espectro visible al tiempo que permite transmitir otras longitudes de onda visibles, principalmente las de la región rojo-amarilla. Es por ello que las zanahorias son de color naranja.
El sistema pi conjugado en 4-metil-3-penten-2-ona da lugar a una fuerte absorbancia UV a 236 nm debido a una transición π - π *. Sin embargo, esta molécula también absorbe a 314 nm. Esta segunda absorbancia se debe a la transición de un electrón sin enlace (par solitario) en el oxígeno hasta un MO antienlace π *:
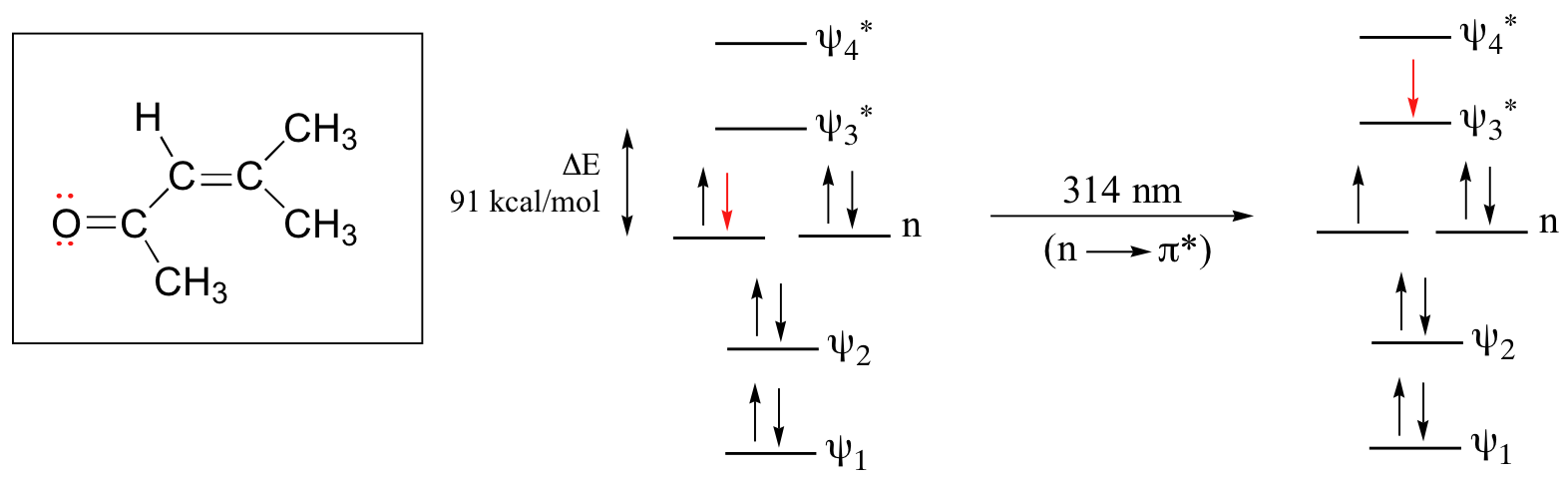
Esto se conoce como una transición n - π *. Los MO no enlazantes (n) son más altos en energía que los orbitales p de unión más altos, por lo que la brecha de energía para una\(n \rightarrow \pi^*\) transición es menor que la de una transición π - π * — y así el pico n - π * está a una longitud de onda más larga. En general, las transiciones n - π * son más débiles (menos luz absorbida) que las debidas a las transiciones π - π *.
¿Cuál es la energía de los fotones (en kJ/mol) de luz con longitud de onda de 470 nm, el l max de b -caroteno?
Ejercicio 4.10
¿Cuál de las siguientes moléculas esperaría absorber a una longitud de onda más larga en la región UV del espectro electromagnético? Explica tu respuesta.
Soluciones
La piel humana puede dañarse por la exposición a la luz ultravioleta del sol. Naturalmente producimos un pigmento, llamado melanina, que protege la piel absorbiendo gran parte de la radiación ultravioleta. La melanina es un polímero complejo, dos de las unidades monoméricas más comunes del cual se muestran a continuación.
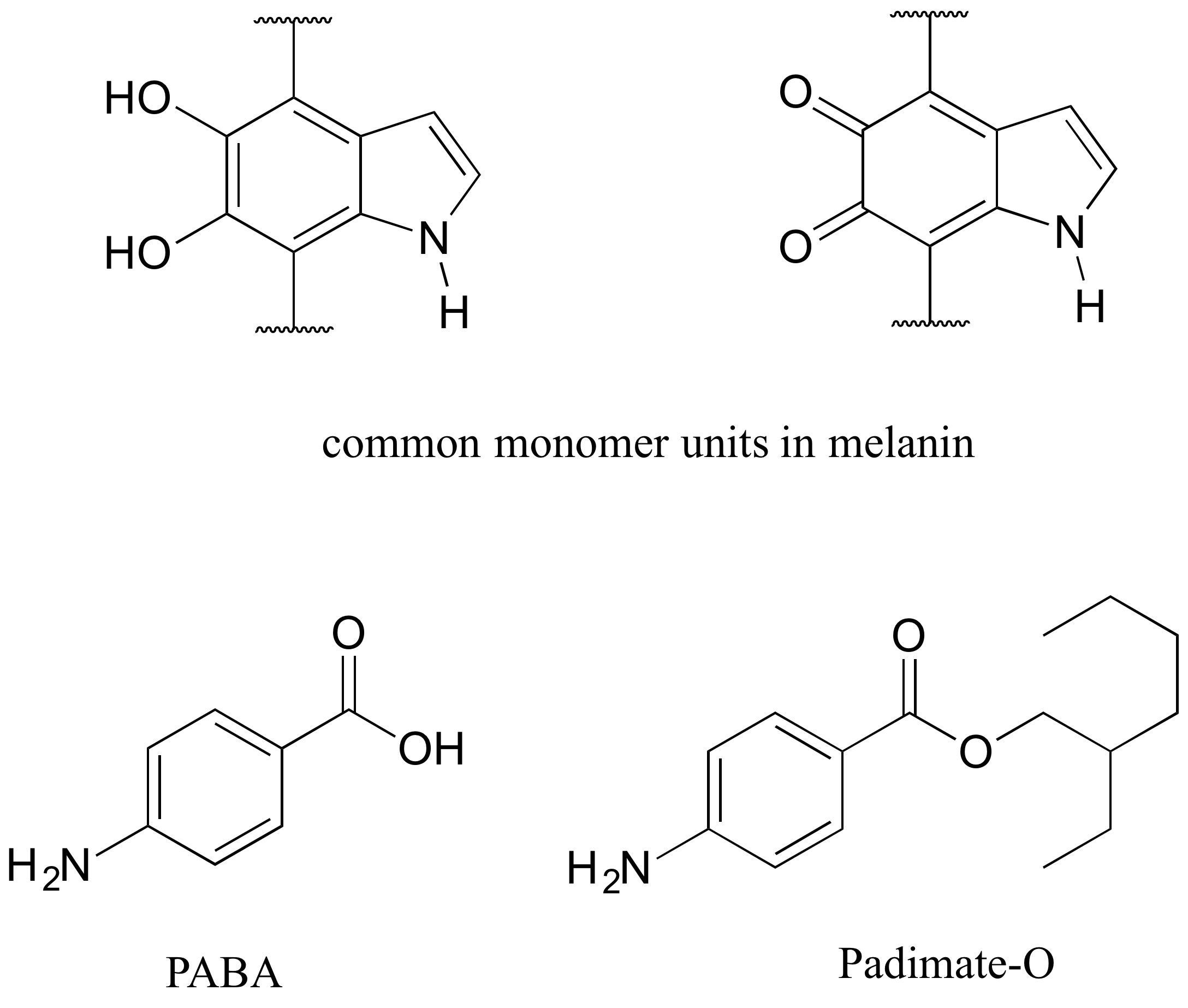
La sobreexposición al sol sigue siendo peligrosa, porque hay un límite en la cantidad de radiación que puede absorber nuestra melanina. La mayoría de los protectores solares comerciales afirman ofrecer protección adicional contra la radiación UV-A y UV-B: UV-A se refiere a longitudes de onda entre 315-400 nm, UV-B a longitudes de onda más cortas y dañinas entre 280-315 nm. El PABA (ácido para-aminobenzoico) se utilizó en protectores solares en el pasado, pero su polaridad relativamente alta significó que no era muy soluble en lociones oleosas, y tendía a enjuagarse al nadar. Muchos protectores solares hoy en día contienen, entre otros ingredientes activos, un derivado más hidrofóbico de PABA llamado Padimate O.
Mirando los espectros UV-Vis
Hemos estado hablando en términos generales sobre cómo las moléculas absorben la luz UV y la luz visible; ahora veamos algunos ejemplos reales de datos de un espectrofotómetro de absorbancia UV-Vis. La configuración básica es la misma que para la espectroscopia IR: la radiación con un rango de longitudes de onda se dirige a través de una muestra de interés, y un detector registra qué longitudes de onda fueron absorbidas y en qué medida ocurrió la absorción.
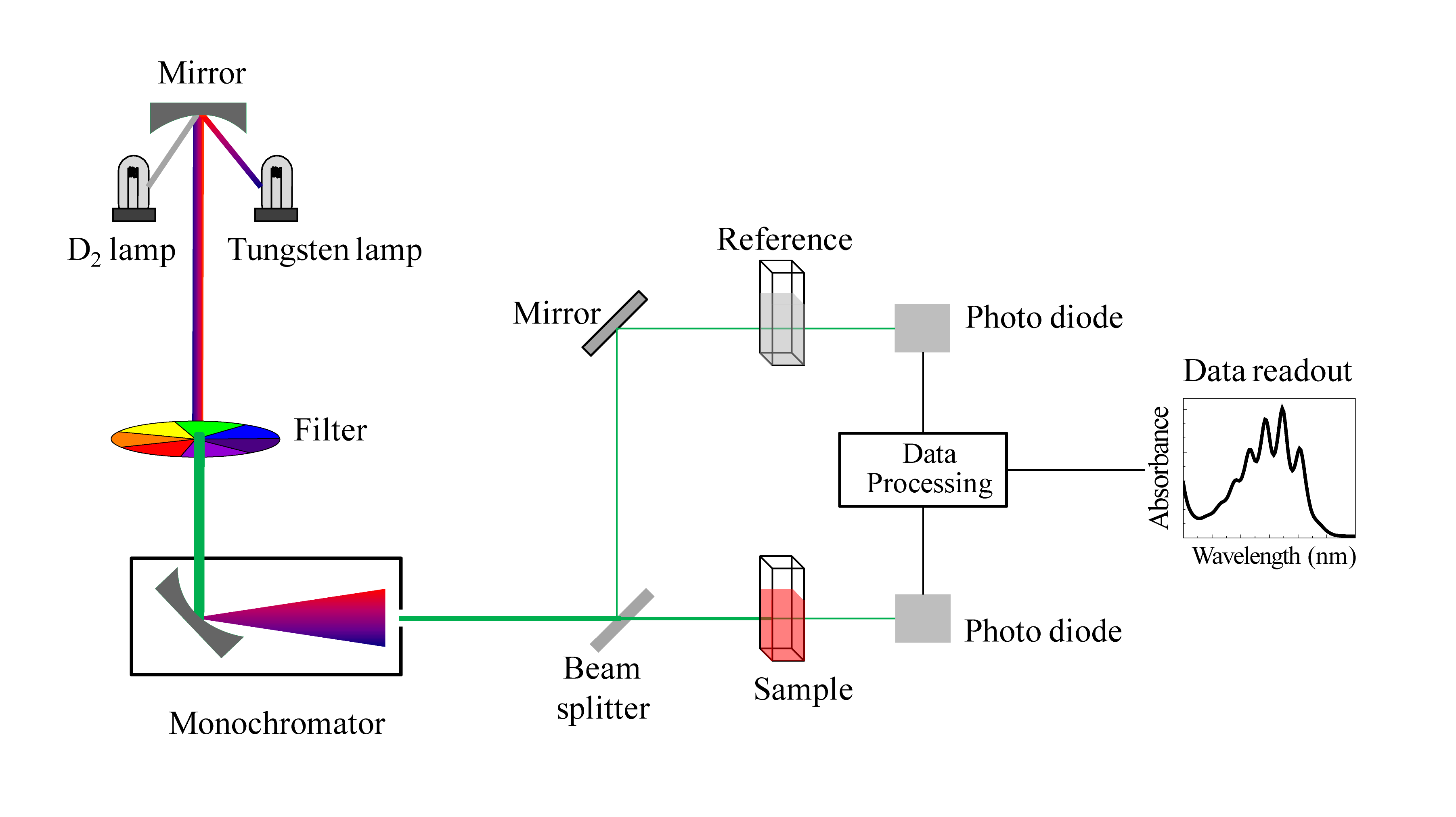 Esquema para un espectrofotómetro UV-Vis
Esquema para un espectrofotómetro UV-Vis
(Imagen de Wikipedia Commons)
A continuación se muestra el espectro de absorbancia de una importante molécula biológica llamada nicotinamida adenina dinucleótido, abreviado NAD +. Este compuesto absorbe la luz en el rango UV debido a la presencia de sistemas de unión pi conjugados.
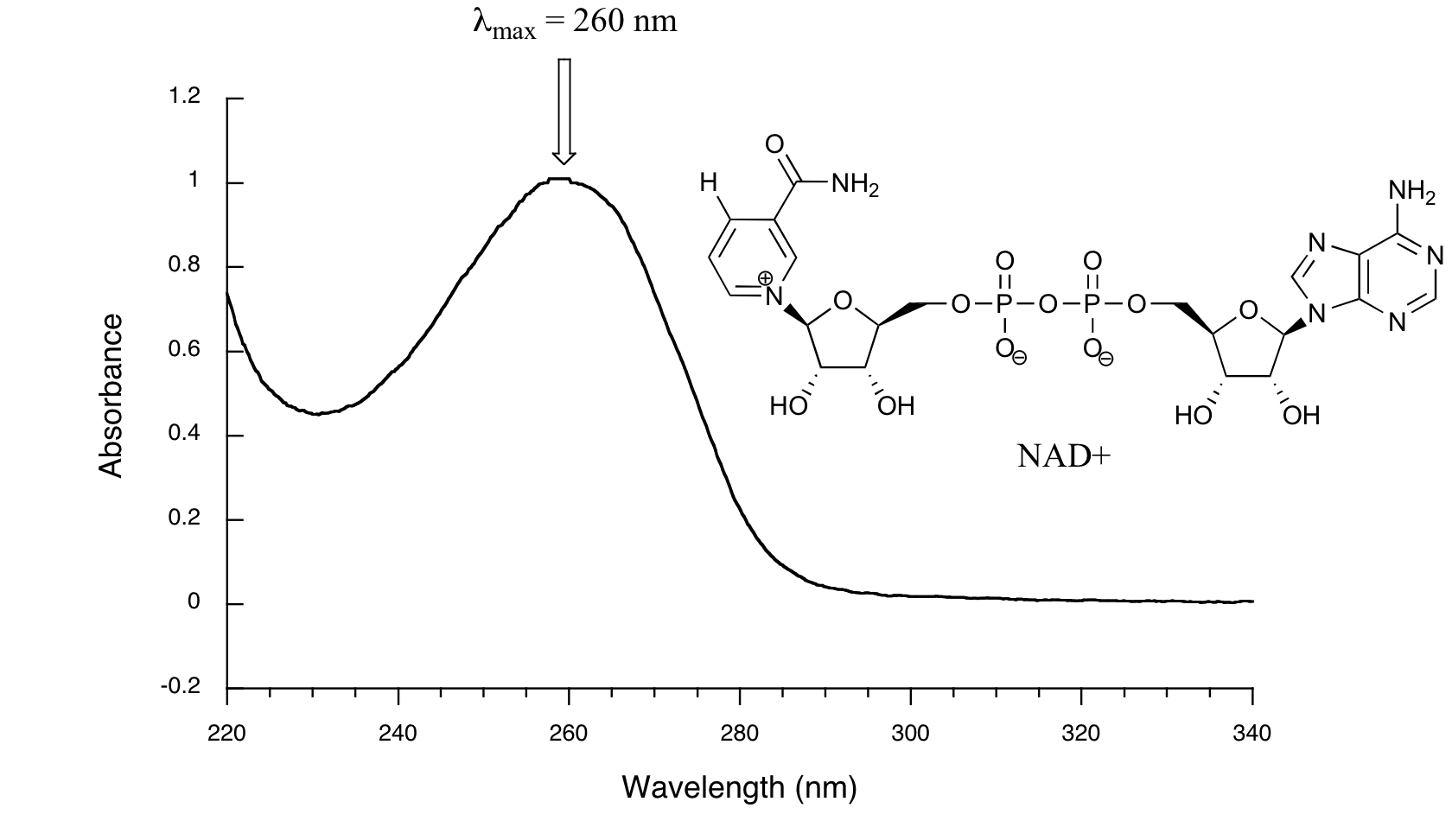
Notarás que este espectro UV es mucho más sencillo que los espectros IR que vimos antes: este solo tiene un pico, aunque muchas moléculas tienen más de uno. Observe también que la convención en espectroscopía UV-Vis es mostrar la línea base en la parte inferior de la gráfica con los picos apuntando hacia arriba. Los valores de longitud de onda en el eje x generalmente se miden en nanómetros (nm) en lugar de en cm -1 como es la convención en espectroscopia IR.
Los picos en los espectros UV tienden a ser bastante amplios, a menudo abarcando más de 20 nm a la altura media máxima. Por lo general, hay dos cosas que buscamos y grabamos a partir de un espectro UV-Vis. La primera es\(\lambda_{max}\), que es la longitud de onda a la máxima absorbancia de luz. Como se puede ver, NAD + tiene\(\lambda_{max} = 260\;nm\). También queremos registrar en cuánta luz se absorbe\(\lambda_{max}\). Aquí utilizamos un número sin unidad llamado absorbancia, abreviado 'A'. Esta contiene la misma información que el número de 'porcentaje de transmitancia' utilizado en la espectroscopia IR, solo expresado en términos ligeramente diferentes. Para calcular la absorbancia a una longitud de onda dada, la computadora en el espectrofotómetro simplemente toma la intensidad de la luz a esa longitud de onda antes de que pase a través de la muestra (I 0), divide este valor por la intensidad de la misma longitud de onda después de que pase por el muestra (I), luego toma el log 10 de ese número:
\[A = \log \dfrac{I_0}{I} \tag{4.3.1}\]
Se puede ver que el valor de absorbancia a 260 nm (A 260) es de aproximadamente 1.0 en este espectro.
Ejercicio 4.11
Expreso A = 1.0 en términos de porcentaje de transmitancia (%T, la unidad utilizada generalmente en espectroscopía IR (y a veces también en UV-Vis).
Soluciones
Aquí está el espectro de absorbancia del colorante alimentario común Rojo #3:
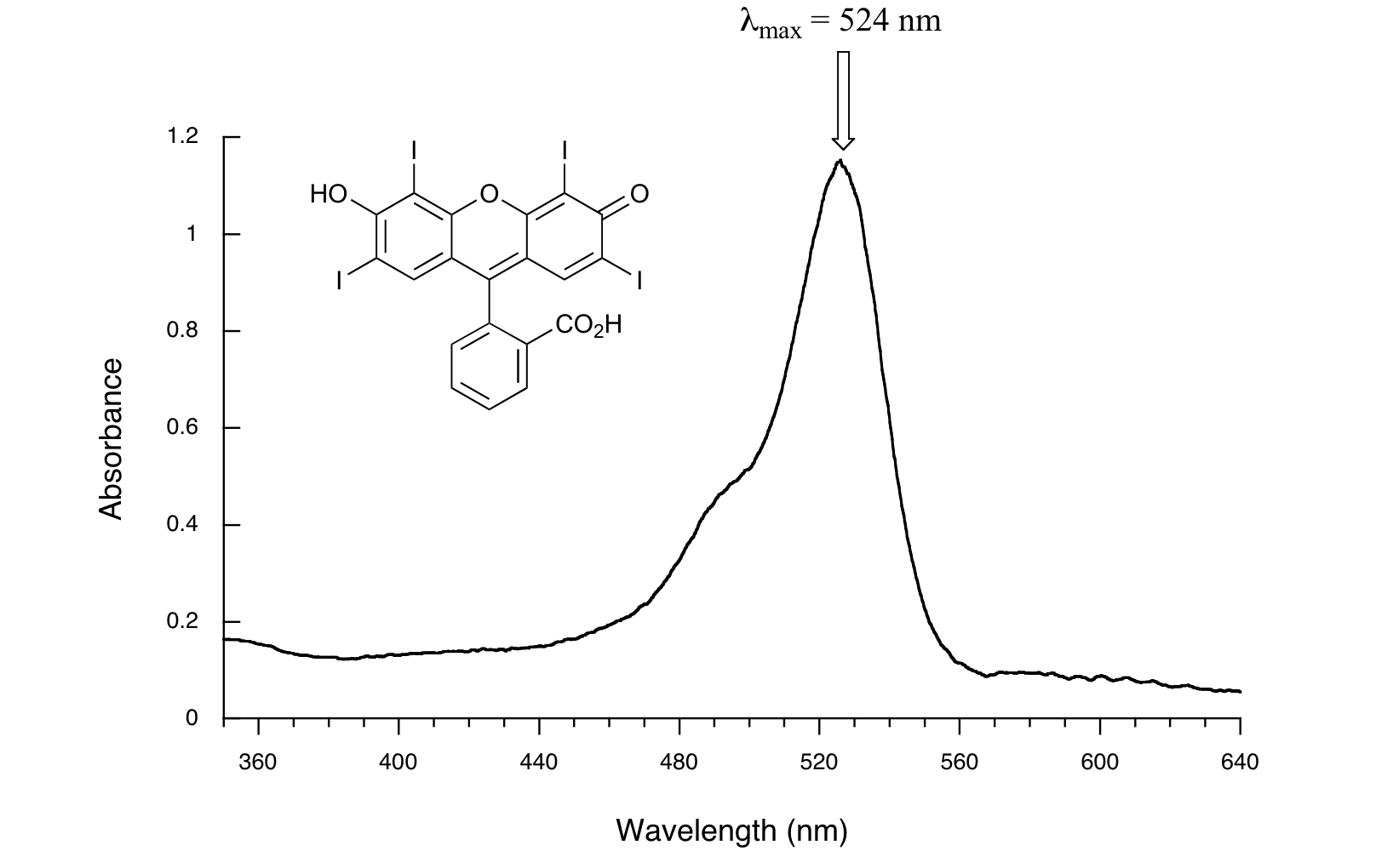
Aquí, vemos que el sistema extendido de enlaces pi conjugados hace que la molécula absorba luz en el rango visible. Debido a que el λ max de 524 nm cae dentro de la región verde del espectro, el compuesto aparece rojo a nuestros ojos. Ahora, echa un vistazo al espectro de otro colorante alimentario, Azul #1:
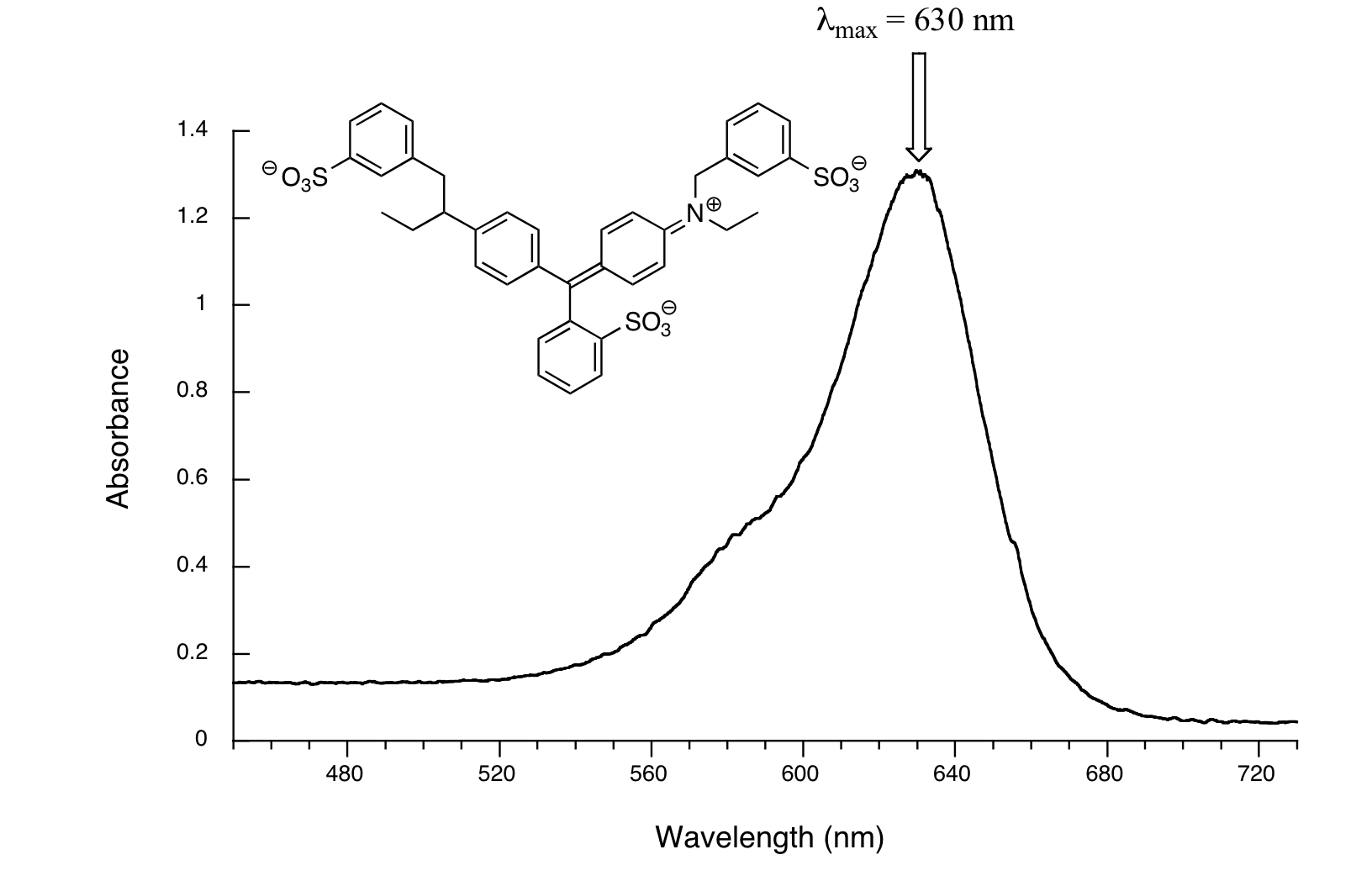
Aquí, la absorbancia máxima está a 630 nm, en el rango naranja del espectro visible, y el compuesto aparece azul.
Aplicaciones de la espectroscopia UV en química orgánica y biológica
La espectroscopia UV-Vis tiene muchas aplicaciones diferentes en química orgánica y biológica. Una de las aplicaciones más básicas es el uso de la Ley Beer - Lambert para determinar la concentración de un cromóforo. Lo más probable es que hayas realizado un experimento Beer — Lambert en un laboratorio de química anterior. La ley es simplemente una aplicación de la observación de que, dentro de ciertos rangos, la absorbancia de un cromóforo a una longitud de onda dada varía de manera lineal con su concentración: cuanto mayor es la concentración de la molécula, mayor es su absorbancia.
Si dividimos el valor observado de A a λ max por la concentración de la muestra (c, en mol/L), obtenemos la absortividad molar, o coeficiente de extinción (ε), que es un valor característico para un compuesto dado.
\[\epsilon = \dfrac{A}{c} \tag{4.3.2}\]
La absorbancia también dependerá, por supuesto, de la longitud de la trayectoria, es decir, la distancia que recorra el haz de luz a través de la muestra. En la mayoría de los casos, los portamuestras están diseñados de manera que la longitud de la trayectoria sea igual a 1 cm, por lo que las unidades para la absortividad molar son L * mol -1 * cm -1. Si buscamos el valor de e para nuestro compuesto a λ max, y medimos la absorbancia a esta longitud de onda, podemos calcular fácilmente la concentración de nuestra muestra. Como ejemplo, para NAD + el valor bibliográfico de ε a 260 nm es de 18,000 L * mol -1 * cm -1. En nuestro espectro NAD + observamos A 260 = 1.0, por lo que usando la ecuación 4.4 y resolviendo para concentración encontramos que nuestra muestra es 5.6 x 10 -5 M.
Las bases de ADN y ARN son buenos cromóforos:

Los bioquímicos y biólogos moleculares a menudo determinan la concentración de una muestra de ADN asumiendo un valor promedio de ε = 0.020 ng -1 ×mL para ADN bicatenario a su λ max de 260 nm (observe que la concentración en esta aplicación se expresa en masa/volumen en lugar de molaridad: ng/mL es a menudo una unidad conveniente para la concentración de ADN cuando se realiza biología molecular).
Debido a que el coeficiente de extinción del ADN bicatenario es ligeramente inferior al del ADN monocatenario, podemos usar la espectroscopia UV para monitorear un proceso conocido como fusión del ADN. Si un tramo corto de ADN bicatenario se calienta gradualmente, comenzará a 'fundirse', o romperse, a medida que aumenta la temperatura (recordemos que dos cadenas de ADN se mantienen unidas por un patrón específico de enlaces de hidrógeno formados por 'emparejamiento de bases').
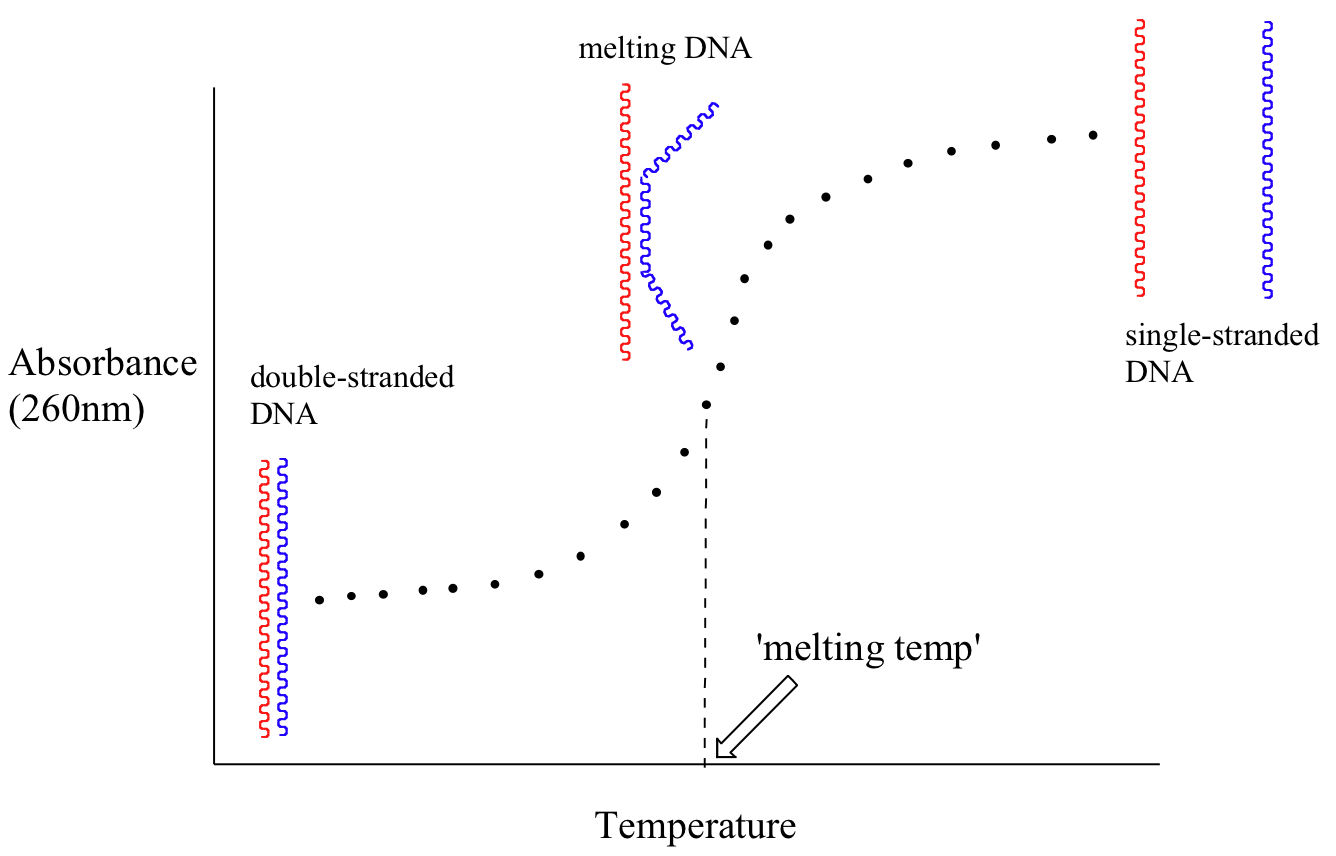
A medida que avanza la fusión, el valor de absorbancia para la muestra aumenta, alcanzando finalmente una meseta alta a medida que todo el ADN bicatenario se rompe, o “se funde”. El punto medio de este proceso, llamado la 'temperatura de fusión', proporciona una buena indicación de cuán fuertemente las dos cadenas de ADN son capaces de unirse entre sí.
Posteriormente veremos cómo la Ley Beer - Lambert y la espectroscopia UV nos proporcionan una manera conveniente de seguir el progreso de muchas reacciones enzimáticas redox (oxidación-reducción) diferentes. En bioquímica, la oxidación de una molécula orgánica a menudo ocurre simultáneamente con la reducción del dinucleótido de nicotinamida adenina (NAD +, el compuesto cuyo espectro vimos anteriormente en esta sección) a NADH:
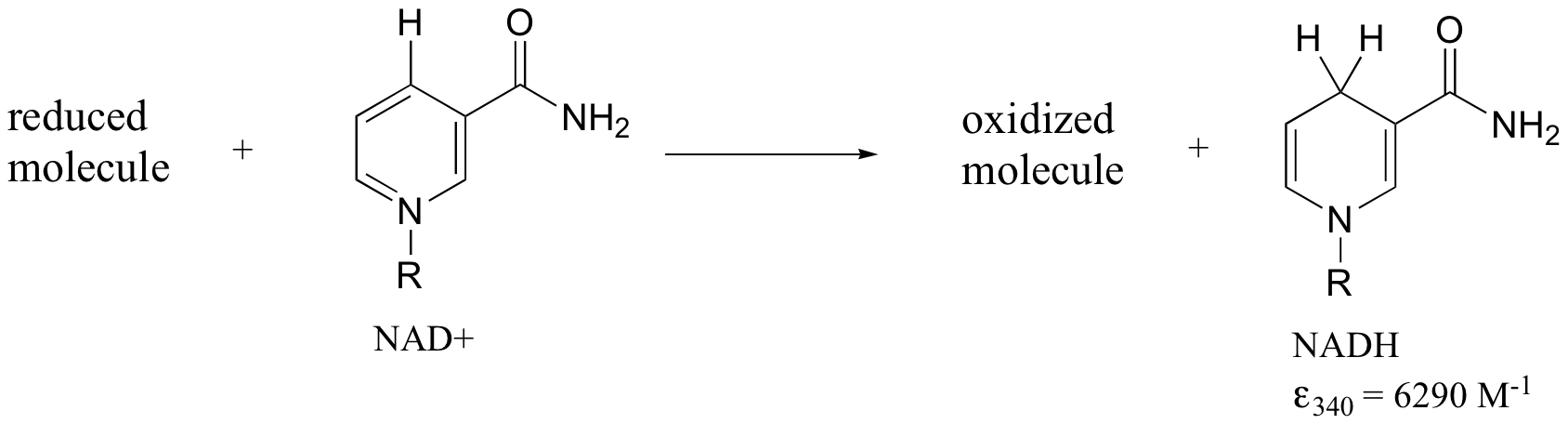
Tanto el NAD + como el NADH absorben a 260 nm. Sin embargo, el NADH, a diferencia del NAD +, tiene una segunda banda de absorbancia con λ max = 340 nm y ε = 6290 L * mol -1 * cm -1. La siguiente figura muestra los espectros de ambos compuestos superpuestos, con el espectro NADH ligeramente desplazado en el eje y:
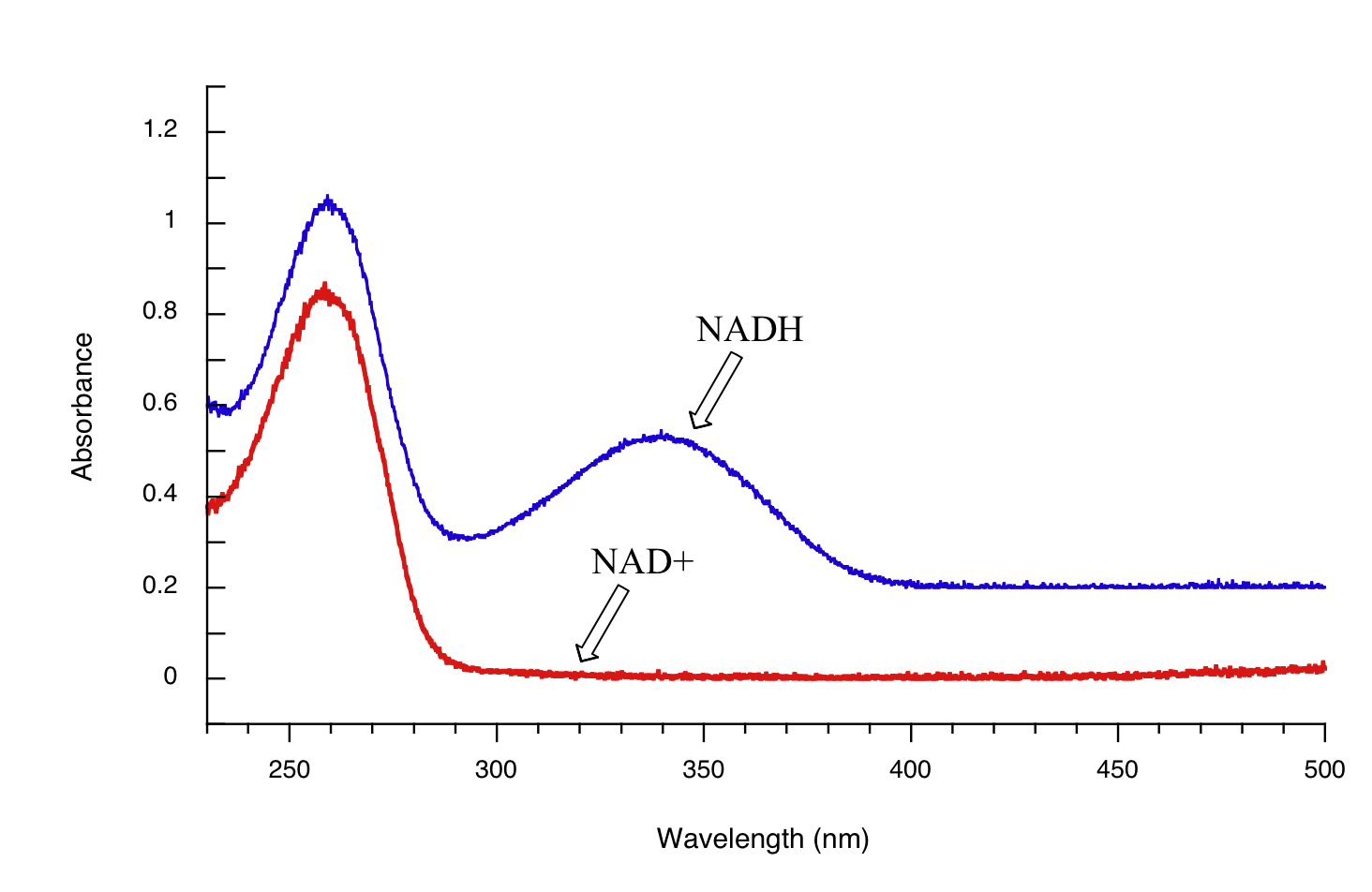
Al monitorear la absorbancia de una mezcla de reacción a 340 nm, podemos 'observar' que se forma NADH a medida que avanza la reacción, y calcular la velocidad de la reacción.
La espectroscopia UV también es muy útil en el estudio de las proteínas. Las proteínas absorben la luz en el rango UV debido a la presencia de los aminoácidos aromáticos triptófano, fenilalanina y tirosina, todos los cuales son cromóforos.
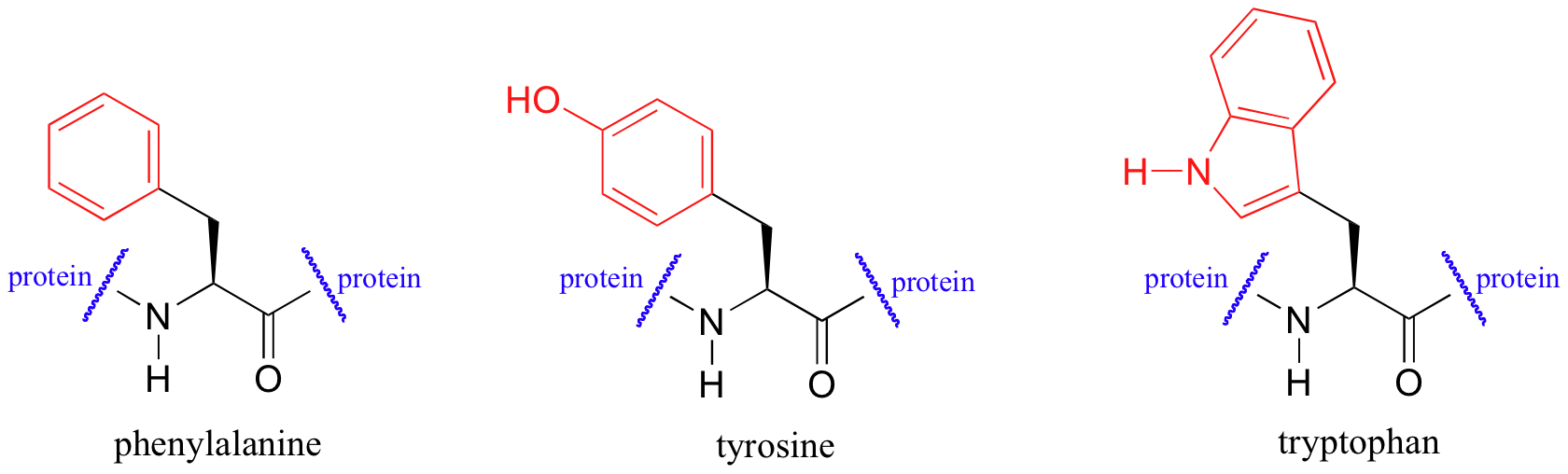
Los bioquímicos suelen utilizar la espectroscopia UV para estudiar los cambios conformacionales en las proteínas, cómo cambian de forma en respuesta a diferentes condiciones. Cuando una proteína sufre un cambio conformacional (despliegue parcial, por ejemplo), el cambio resultante en el ambiente alrededor de un cromóforo de aminoácido aromático puede provocar que se altere su espectro UV.
Tutoriales en video de Khan Academy sobre espectroscopia UV-Vis


